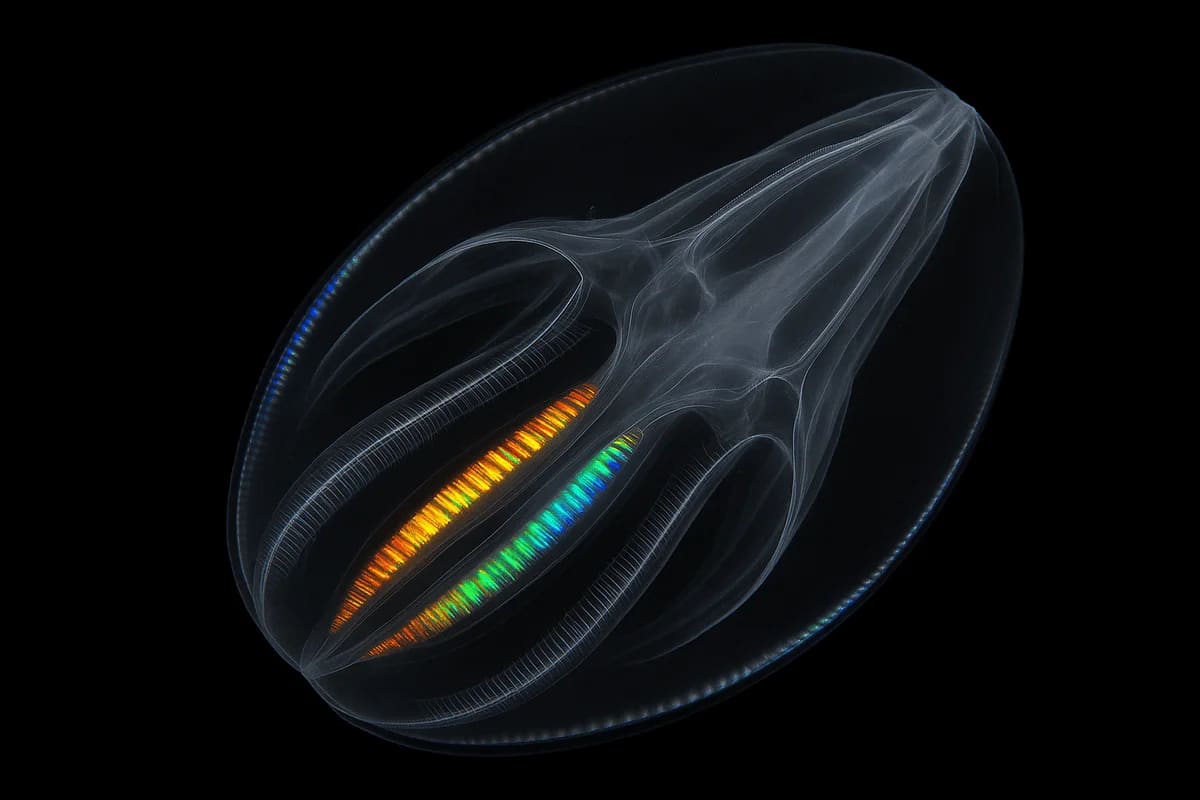
La capacidad de activar o silenciar genes a distancia no es una invención reciente de organismos complejos. Un nuevo estudio publicado en la revista Nature por investigadores del Centro de Regulación Genómica (CRG) y el Centro Nacional de Análisis Genómico (CNAG) demuestra que la regulación genética distal, basada en el plegado del ADN en bucles tridimensionales, surgió entre 650 y 700 millones de años atrás, en los orígenes de la vida animal.
Este tipo de regulación permite que regiones del ADN ubicadas lejos de un gen puedan controlar su actividad, lo cual es fundamental para desarrollar tejidos especializados y tipos celulares distintos sin necesidad de crear genes nuevos. Según los autores, este mecanismo probablemente apareció en un organismo marino ancestral común a todos los animales actuales, mucho antes de lo que se pensaba.
La investigación, liderada por la Dra. Iana Kim (CRG y CNAG), utilizó la técnica Micro-C para mapear el ADN en 3D en once especies, incluyendo medusas peine como Mnemiopsis leidyi (la conocida 'nuez de mar'), esponjas, placozoos y cnidarios. Tan solo Mnemiopsis mostró más de 4.000 bucles en su genoma, compuesto por unos 200 millones de letras, una proporción sorprendente considerando su simplicidad evolutiva.
“Esta criatura podía reutilizar su conjunto de herramientas genéticas de diferentes maneras, como si fuera una navaja suiza”, explica Kim. Esto le habría permitido a los primeros animales explorar nuevas estrategias de supervivencia con una caja de herramientas genética flexible y compleja, ya desde el inicio de la evolución multicelular.
Uno de los hallazgos más reveladores es que los parientes unicelulares de los animales no presentan este tipo de regulación. Solo los animales de ramificación temprana como las medusas peine y los cnidarios mostraron estos bucles, lo que sitúa el origen de la regulación distal mucho antes del ancestro de los bilaterales, que se estimaba hace 500 millones de años.
En los vertebrados actuales, los bucles están organizados por una proteína llamada CTCF, clave en la arquitectura del genoma. Sin embargo, los animales estudiados en este trabajo no poseen dicha proteína. En cambio, las medusas peine usan otra proteína de la misma familia estructural para generar bucles, lo que demuestra que existen mecanismos alternativos de regulación compleja.

“Es impresionante que la evolución haya resuelto el mismo problema con herramientas diferentes”, afirma el profesor Marc A. Marti-Renom, del CNAG y CRG. Esto derriba la suposición de que CTCF era imprescindible para la regulación distal y abre nuevas vías para entender la diversidad evolutiva en el control del genoma.
Comprender cómo surgieron estos sistemas en animales tan antiguos también tiene implicaciones modernas. La misma lógica de bucles genéticos que usan las medusas peine es la que permite a nuestras células humanas desarrollar desde neuronas hasta glóbulos blancos. Cuando estos contactos tridimensionales fallan, pueden aparecer enfermedades. Estudiar su origen permite anticipar dónde el sistema es robusto y dónde puede fallar, una información clave para la medicina del futuro.
El estudio fue realizado por el Centro de Regulación Genómica (CRG), el Centro Nacional de Análisis Genómico (CNAG), la Universidad de Bergen, la Queen Mary University of London, la Universidad Prefectural de Hiroshima y la Universidad de Alberta, con financiación del Consejo Europeo de Investigación.
Referencias: Nature, Centro de Regulación Genómica.